Das Ausleuchten des Genoms
Eine neue CRISPR/Cas9 basierte molekulare Visualisierungsmethode
Seit der Vorstellung des CRISPR/Cas9-Systems im Jahr 2012 schlägt die molekularbiologische Technologie Wellen in der Wissenschaftswelt. Forscher haben sich die Schneidefähigkeiten des Cas9-Proteins zunutze gemacht und bereits diverse Anwendungen für die sogenannte Genschere entwickelt. Forscher des Leibniz-Instituts für Pflanzengenetik und Kulturpflanzenforschung (IPK) Gatersleben haben nun eine etwas andersartige Anwendung für den RNA/Protein-Komplex gefunden – als zytogenetische Taschenlampe.
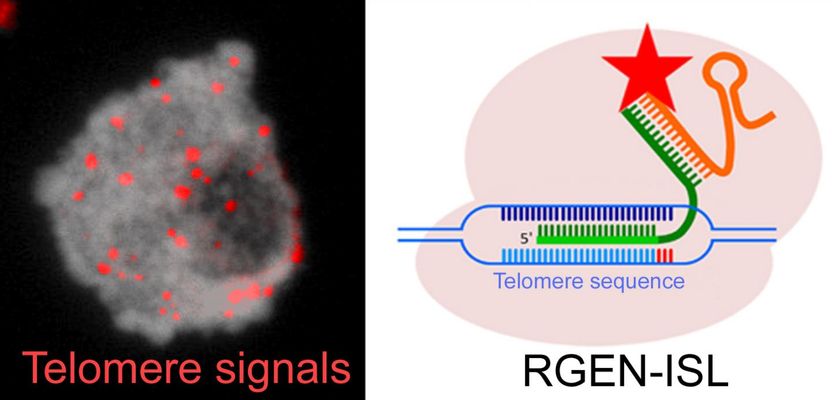
Zellkern der Augenbohne mit Telomer-spezifischen Signalen (in rot), welche mit Hilfe der CRISPR/Cas9-basierten REGN-ISL Methode detektiert wurden.
Takayoshi Ishii, Andreas Houben
Im Gegensatz zur herkömmlichen in-situ Hybridisierung wird die DNA bei der Benutzung des neuen RNA-guided endonuclease - in situ labelling-Werkzeugs (RGEN-ISL) nicht denaturiert. Folglich bleibt das Chromatin unbeschädigt und somit kann die Chromatinstruktur nun auch untersucht werden. Des Weiteren ist RGEN-ISL mit Protein-Nachweismethoden kombinierbar und ermöglicht die Echtzeitvisualisierung des Markierungsprozesses. Ursprünglich wurde die neue Methode für Pflanzengenome entwickelt, jedoch kann RGEN-ISL vermutlich in allen Organismen verwendet werden und stellt ein vielversprechendes, neues Werkzeug im Gebiet der Chromosomenbiologie, einschließlich der Medizin, dar.
Die Entdeckung des CRISPR/Cas9-Systems gilt als ein Meilenstein im Gebiet des gezielten Genome Editings. Der RNA/Protein-Komplex, dessen Name kurz für Type II Clustered Regularly Interspaced Short Palindromic Repeats-associated Caspase 9 steht, stammt ursprünglich von der Bakterie Streptococcus pyogenes und ist inzwischen ein etabliertes Werkzeug für das gezielte Editieren von eukaryotischen Genomen.
Während die scherenartigen Eigenschaften des molekularbiologischen Systems bereits in einer Vielzahl von Anwendungen eingesetzt werden, verwenden Forscher des Leibniz-Instituts für Pflanzengenetik und Kulturpflanzenforschung (IPK Gatersleben) CRISPR/Cas9 nun, um Licht in das eukaryotische Genom zu bringen - mit einer neuen zytogenetischen Methode, RNA-guided endonuclease - in situ labelling (RGEN-ISL).
In den letzten 30 Jahren war Fluoreszenz in situ Hybridisierung (FISH) die etablierte und übliche Methode, um in-situ DNA-Sequenzen auf chromosomaler Ebene zu visualisieren. Jedoch setzt die Anwendung von FISH die Denaturierung der zu untersuchenden DNA voraus, was oft zur Schädigung der Chromatinstruktur führt.
Indem die IPK-Forscher die RGEN-ISL-Methode auf CRISPR/Cas9 basierten, konnten sie nun den Denaturierungsschritt umgehen. Zugleich konnten sie die gewünschten Fluoreszenzmarkierungseigenschaften der konventionellen FISHMethode in ihre neue zytogenetische Methode integrieren. Da die Anwendung von RGEN-ISL die Chromatinstruktur schont, ermöglicht sie nun die Untersuchung der räumlich-zeitlichen Struktur des Genoms.
Weitere Experimente zeigten, dass RGEN-ISL die Leistungen herkömmlicher Methodenkombinationen, beispielsweise von FISH und Immunhistochemie, übertrifft. So ist die benötigte Vorbereitung geringer und die neue Methode zudem vergleichsweise schneller und günstiger. Wichtig ist, dass RGEN-ISL bei einer Temperaturspanne von 4 °C bis 37 °C funktioniert und mit zusätzlichen Proteindetektions- und bildgebenden Methoden kombiniert werden kann. Ein weiterer Bonus ist, dass RGEN-ISL die Echtzeitvisualisierung des CRISPR/Cas9-basierten DNA-Markierungsprozesses ermöglicht und somit die Kinetik der Reaktion mit aufzeigt.
Soweit haben die Forscher RGEN-ISL in pflanzlichen Proben, aber auch in menschlichen Chromosomen, getestet und damit aufgezeigt, dass ihre Methode wahrscheinlich in allen Organismen angewendet werden kann. Derzeit ist die Verwendung von RGEN-ISL auf repetitive DNA-Sequenzen beschränkt, welche beispielsweise oft in Pflanzen gefunden werden. Jedoch glaubt Dr. Takayoshi Ishii, welcher die ursprüngliche Idee für die neue Methode hatte und nun an der Tottori University (Japan) arbeitet, dass RGEN-ISL zukünftig auch für die Visualisierung von Einzelkopie-Sequenzen adaptiert werden kann.

























































